 View full size
View full size
- Analiza kwasów nukleinowych
- Analiza białek
- Odczynniki biochemiczne
- Enzymy
- Edytowanie genów
- Klonowanie
- Diagnostyka kliniczna
- Sprzęt laboratoryjny
- Oprogramowanie
- Download
- A&A Biotechnology
Aktualności
 View full size
View full size
Metoda detekcji: NGS
Kompleksowe rozwiązanie – od DNA do raportu klinicznego
Solidny panel diagnostyczny - regiony hotspot dla wielu genów diagnostycznych
Łatwy do użycia – brak potrzeby wcześniejszego doświadczenia w technikach NGS oraz doświadczenia bioinformatycznegono
Zestaw służy do diagnozowania raka jelita grubego oraz raka płuc z DNA wyizolowanego z FFPE. Zawiera panel wybranych obszarów hot-spotów, w których objawiają się mutacje decydujące o kierunku dalszego leczenia. Najważniejsze są mutacje w genach KRAS, NRAS i BRAF, w przypadku zmutowanych genów pacjent nie odnosi korzyści z leczenia anty-EGFR. Zestaw służy do przygotowania biblioteki próbek do sekwencjonowania na instrumencie Miseq i jest metodą sekwencjonowania amplikonu. Zestaw zawiera bezpłatne oprogramowanie do oceny ERMI. To oprogramowanie jest bardzo przyjazne dla użytkownika i nie wymaga żadnej wiedzy bioinformatycznej.
Próbki DNA przygotowuje się w dwuetapowej amplifikacji PCR. Docelowe regiony hotspot są amplifikowane podczas pierwszej multipleksowej reakcji PCR, a specyficzne dla próbki molekularne kody kreskowe są dodawane w drugiej uniwersalnej amplifikacji PCR. Poszczególne próbki biblioteki są oczyszczane, normalizowane, łączone i sekwencjonowane na platformie Illumina MiSeq®. Dane z sekwencjonowania są przetwarzane i analizowane przez oprogramowanie ERMI, a użytkownik może eksportować raport.
Parametry zestawu diagnostycznego
- Zestawy diagnostyczne do sekwencjonowania nowej generacji na platformie Illumina MiSeq®
- Do 64 próbek na cykl sekwencyjny (przy użyciu chemii v2 300 cykli)
- Panel 8 odpowiednich genów do diagnostyki molekularnej mutacji somatycznych w raku jelita grubego, raku płuc i czerniakach z zastosowaniem terapii przeciwciałem anty-EGFR
- Starannie zaprojektowane primery do przygotowania pojedynczej probówki amplikonu do multipleksowej reakcji PCR zapewniające jednolite pokrycie
- Odpowiedni dla próbek FFPE i DNA wejściowego w ilościach zaledwie 20 ng
- Prosty protokół przygotowania biblioteki z krótkim czasem pracy
- Opracowany we współpracy z ekspertami z Kliniki Onkologii, General University Hospital in Prague
- Bioinformatyczne oprogramowanie zapewnia przyjazną dla użytkownika analizę danych i generuje raport
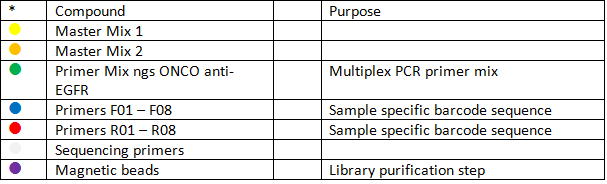
Panel genów w zestawie diagnostycznym ONCO Anti-EGFR:
|
KRAS |
chr 12 |
exon 3 |
exon 2 |
exon 4 |
|
|
BRAF |
chr 7 |
exon 11 |
exon 15 |
||
|
NRAS |
chr 1 |
exon 2 |
exon 3 |
exon 4 |
|
|
EGFR |
chr 7 |
exon 18 |
exon 19 |
exon 20 |
exon 21 |
|
PIK3CA |
chr 3 |
exon 21 |
|||
|
AKT1 |
chr 14 |
exon 3 |
|||
|
HER2 |
chr 17 |
exon 25 |
|||
|
SMAD |
chr 18 |
exon 12 |


